没有合适的资源?快使用搜索试试~ 我知道了~
资源推荐
资源详情
资源评论

2009 年计算机辅助药物设计和大分子模拟技术暑期培训班 Discovery Studio Tutorials
- 1 -
蛋白质结构预测技术简介
蛋白质结构预测技术简介蛋白质结构预测技术简介
蛋白质结构预测技术简介
简介
简介简介
简介
蛋白质结构的解析对其功能的理解至关重要。然而,由于技术手段的限制,利用实验方
法(主要为 X-ray,NMR)解析蛋白质结构投入大、周期长、风险大。对于某些膜蛋白,只
利用现有技术条件,其结构甚至无法解析。另一方面,随着分子生物学技术的成熟及高通量
测序技术的发展,越来越多的基因序列可以轻松被找到。这造成了现代蛋白质科学中一个奇
怪的现象:蛋白质序列数据的累积量及积累速度远远超过蛋白质结构。这种序列与结构间不
平衡的现象极大地限制了我们对蛋白质功能及其相关作用机理的理解。所以我们需要一种能
够简单、快速且相对准确的技术来确定蛋白质的空间结构。
蛋白质建模技术可以很好的解决上面的问题。该方法利用信息技术的手段,可以直接从
蛋白的一级结构(氨基酸序列)预测蛋白质的高级结构(主要为三级结构)。根据最新一届
国际建模大赛(CASP)的分类,目前主要的蛋白质建模方法包括两种:基于模板的建模
(Template-based Modeling)和自由建模(Free Modeling)。前者又包括两种方法:同源建模
法(Homology Modeling)和“穿线法”(Threading)。后者主要以从头计算法(ab initio)为
主。所有的建模方法中,以同源建模法(Homology Modeling)使用最为广泛,预测结果的准
确性最大。
同源建模的理论基础为蛋白质三级结构的保守性远远超过一级序列的保守性。因此,人
们可以通过使用一个或多个已知结构的蛋白(模板蛋白,template)来构建未知结构蛋白(目
标蛋白,target)的空间结构。其主要的步骤包括:
1. 搜索用于建模的 template(s)
2. 将 target 与 templates 进行比较
3. 将步骤(2)中的比较信息用于建模
Discovery Studio 为用户提供了一整套利用 Homology Modeling 方法自动预测蛋白质空
间结构的工具。用户只需要提供蛋白质的氨基酸序列就可以轻松完成模型构建及模型可信度
评估的工作。DS 的 Homology Modeling 主要基于 MODELER 程序。目前 MODELER 已成
为使用最为广泛,预测最为准确的同源建模工具之一。其主要的建模步骤包括:
1. 使用序列相似性工具 BLAST 或 PSI-BLAST 搜寻目标序列的模板
2. 使用结构比对方法将模板进行比对,叠合
3. 使用序列比对方法将目标序列与模板结构的序列进行比对
4. 使用 MODELLER 产生目标序列的模型
5. 模型的评估
本教程中以一个胞外淀粉酶的模型构建过程为例子,展示如何使用 DS 为该淀粉酶自动构
建空间结构,并对所构建的模型进行评估,帮助大家获得 Homology Modeling 最直观的结果。

2009 年计算机辅助药物设计和大分子模拟技术暑期培训班 Discovery Studio Tutorials
- 2 -
1 识别模板
识别模板识别模板
识别模板,
,,
,比对模板
比对模板比对模板
比对模板
本教程使用 BLAST 来搜索 templates。进行 BLAST 搜索时,数据库可以使用 Protein Data
Bank(PDB)数据库也可以用 PDB_nr95(PDB 非冗余结构数据库)。为缩短搜索时间,本
文使用 PDB_nr95 数据库来寻找模板。
1.1 载入序列
载入序列载入序列
载入序列
从
从从
从 Files Explorer, 打开
打开打开
打开 Samples | Tutorials | Protein Modeling | P41131.fasta.
1.2 BALST PDB_nr95 数据库
数据库数据库
数据库,
,,
,寻找模板
寻找模板寻找模板
寻找模板
1.2.1 选择
选择选择
选择 target
在
在在
在 Protocols Explorer, 展开
展开展开
展开 Sequence Analysis 文件夹
文件夹文件夹
文件夹,
,,
,双击
双击双击
双击 BLAST Search (DS Server).
在
在在
在 the Parameters Explorer, 点击
点击点击
点击 the Input Sequence parameter ,
,,
,选择
选择选择
选择 P41131:P41131
Input Sequence 中的文件名为 sequence window 的名字(P41131)与该窗口中的序列名称
(P41131)的名字组合。
1.2.2 选择
选择选择
选择 BLAST 数据库
数据库数据库
数据库
Input Database 选择
选择选择
选择 PDB_nr95
注意
注意注意
注意:PDB_nr95 序列数据库已经安装在 DS server 上。如果需要 BAST 其它数据库,用户
需要另外安装相应的数据库。
注意
注意注意
注意:如果改动默认参数或使用不同的(或升级版)的 PDB_nr95 数据库,BLAST 结果可
能与本教程的结果不一致。
2009 年计算机辅助药物设计和大分子模拟技术暑期培训班 Discovery Studio Tutorials
- 3 -
1.2.3 运行
运行运行
运行 Protocol
在
在在
在 Protocols toolbar, 点击
点击点击
点击 运行
运行运行
运行,
,,
,等待计算完成
等待计算完成等待计算完成
等待计算完成.
计算完成后,会显示一个“Job Completed”的对话框。点击 OK。
1.2.4 查看计算结果
查看计算结果查看计算结果
查看计算结果
在
在在
在 Jobs Explorer 中
中中
中, 双击
双击双击
双击 job 栏中完成的计算
栏中完成的计算栏中完成的计算
栏中完成的计算——
————
——“ Blast Search DS Server”
这将打开一个 Html 的窗口,里面包含 Reprot.htm 文件(该文件为比对结果报告)
Html 窗口中
窗口中窗口中
窗口中, Output Files 部分
部分部分
部分, 点击
点击点击
点击 the View Results .
这将打开 BLAST 搜索找到的序列
注 意
注 意注 意
注 意 : 由 于 没 有 设 置 结 果 的 保 存 路 径 , BLAST 的 结 果 保 存 于 默 认 文 件 夹 My
Documents\Discovery Studio Client\Results\BLASTSearchDSServer_<time stamp><ID>
在
在在
在 P41131 - Blast 窗口
窗口窗口
窗口, 点击该窗口下的
点击该窗口下的点击该窗口下的
点击该窗口下的 Table View tab。
。。
。
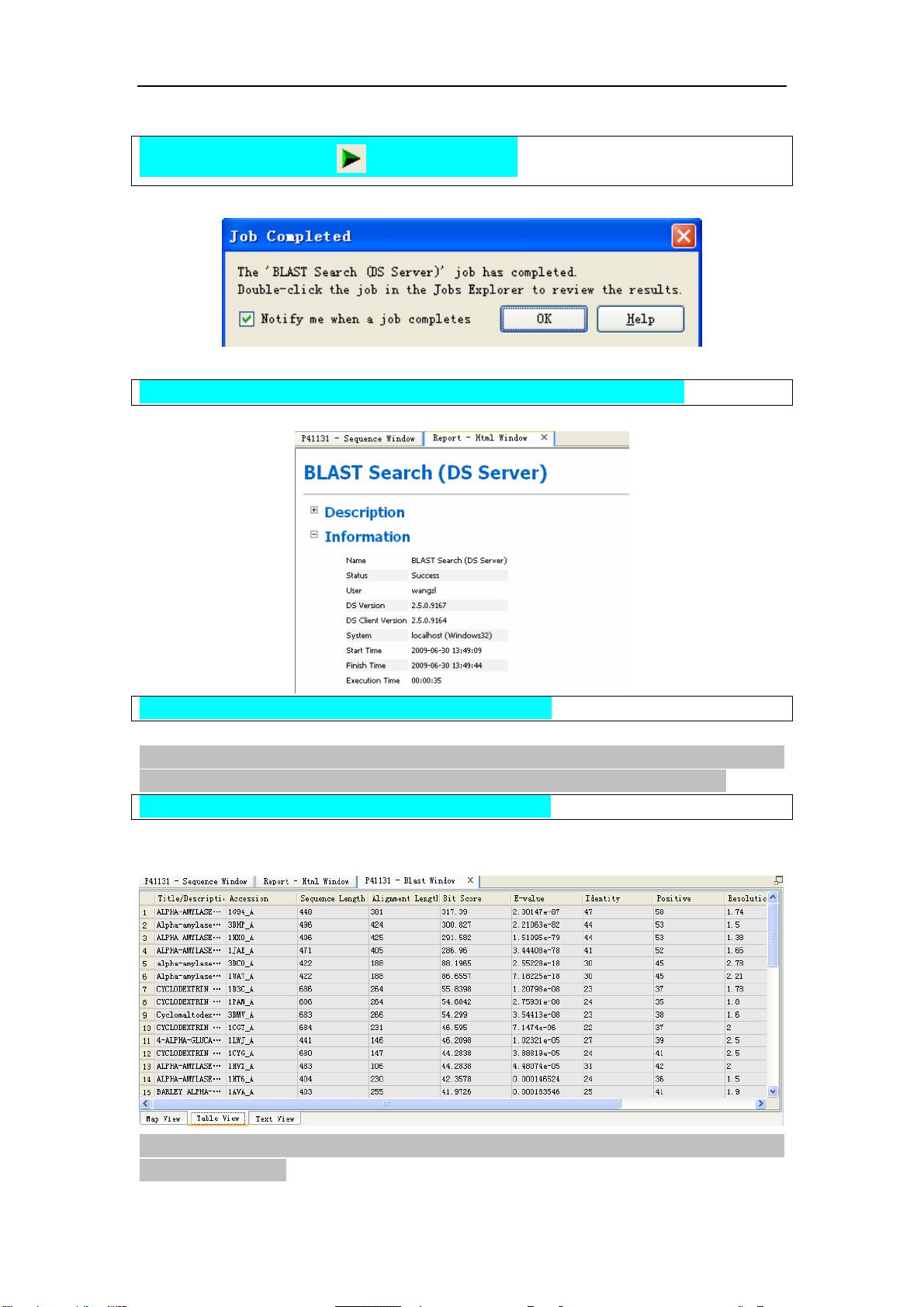
Table View 显示了命中的序列。每行表示一条命中的氨基酸序列。在 DS 中,灰色的 cell 不
能被编辑。
注意
注意注意
注意:命中的序列按照 E 值(序列比对的可行度)进行降序排序。E 值最低的序列,结果最
可靠,排在第一行。
2009 年计算机辅助药物设计和大分子模拟技术暑期培训班 Discovery Studio Tutorials
- 4 -
点击
点击点击
点击 Map View tab.
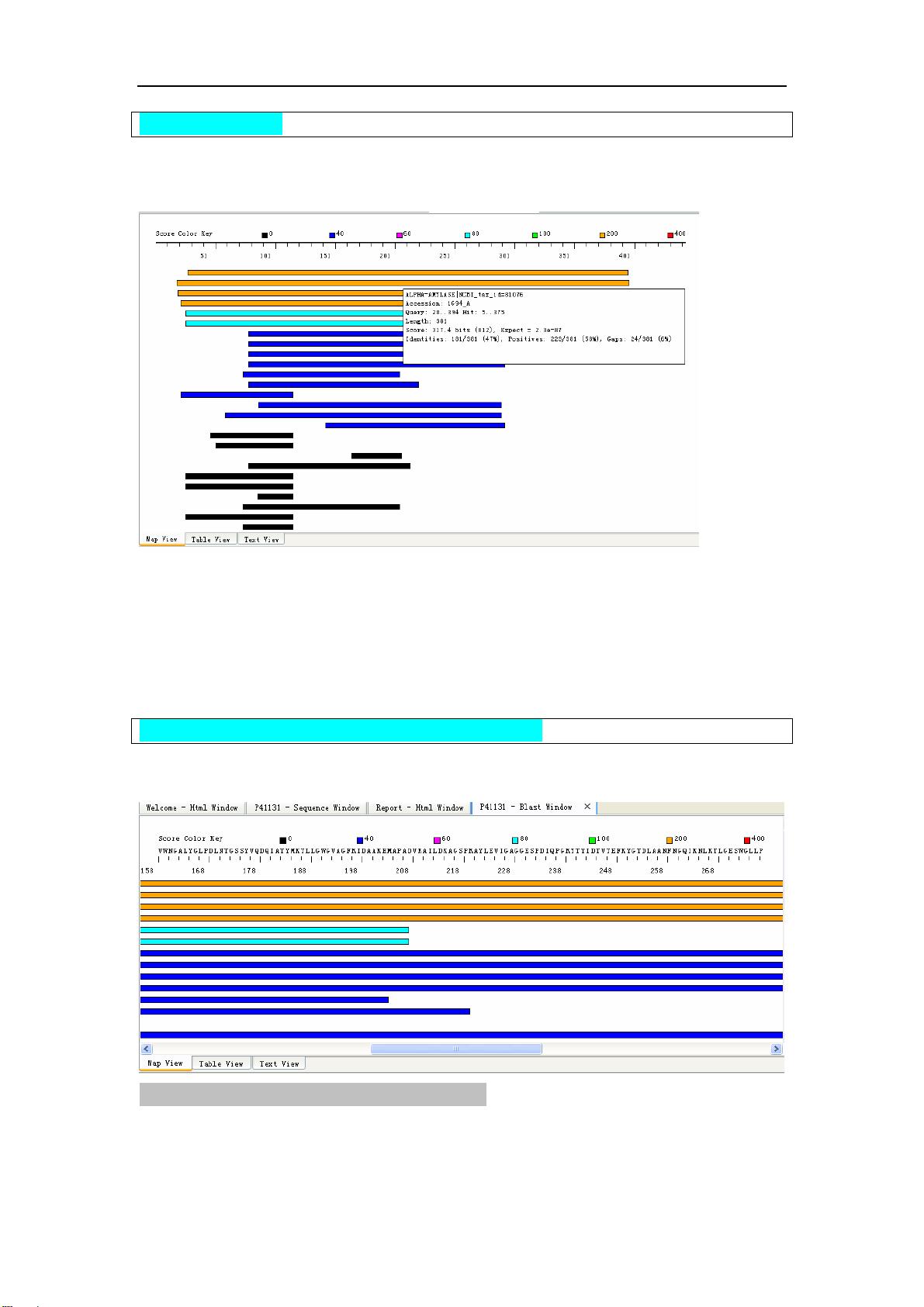
Map View 将命中结果都显示在一张图中,每条线表示一条序列。每根横条根据打分不同而
配以不同的颜色(分数超过 400 为红色,最佳的命中结果)。本例中的 target P41131 放在窗
口的最上方,为一条长度为 443 个氨基酸的直线。
用户可以将鼠标放置在某一个命中序列上,如下信息将会显示(如上图):
序列数据库的描述
序列的编号
目标序列中的起始氨基酸位置
数据库中命中序列的起始氨基酸位置
命中序列的长度
命中序列的分数
滑动鼠标的中间键可以
滑动鼠标的中间键可以滑动鼠标的中间键可以
滑动鼠标的中间键可以放
放放
放大
大大
大(
((
(缩小
缩小缩小
缩小)
))
)Map View 中的结果
中的结果中的结果
中的结果
这时用户可以看到窗口顶端 target 的相应氨基酸。可能需要放大几次才能看见具体的氨基酸
类型。
注意
注意注意
注意:Map view 中命中序列的顺寻并没有改变。
2 将模板进行比对
将模板进行比对将模板进行比对
将模板进行比对
为了构建 target 的 3D 结构,我们需要挑选一个或多个合适的同源模板(templates)。一
2009 年计算机辅助药物设计和大分子模拟技术暑期培训班 Discovery Studio Tutorials
- 5 -
个理想的 template 需要涵盖整个 target 的长度,具有较高的序列等同性(Sequence identity),
并且 E 值要够小(< 1×10
-5
)。根据上述原则,我们选用前 4 个命中序列作为 template。
一般而言,若有多条模板(模板之间相似度不能太高)与 target 具有相似的同源性,那
么我们将使用多模板来构建同源模型。这些模板在核心区域一般都高度保守,而在一些 loop
区的构象上则有所不同。Target 可以与其中某个模板在某 loop 区匹配,而与另一个模板在另
一 loop 区匹配。因此,使用多模板可使建模过程中模型的每个部分都能找到最合适的模板。
2.1 载入模板结构及其与
载入模板结构及其与载入模板结构及其与
载入模板结构及其与 target 的比对结果
的比对结果的比对结果
的比对结果
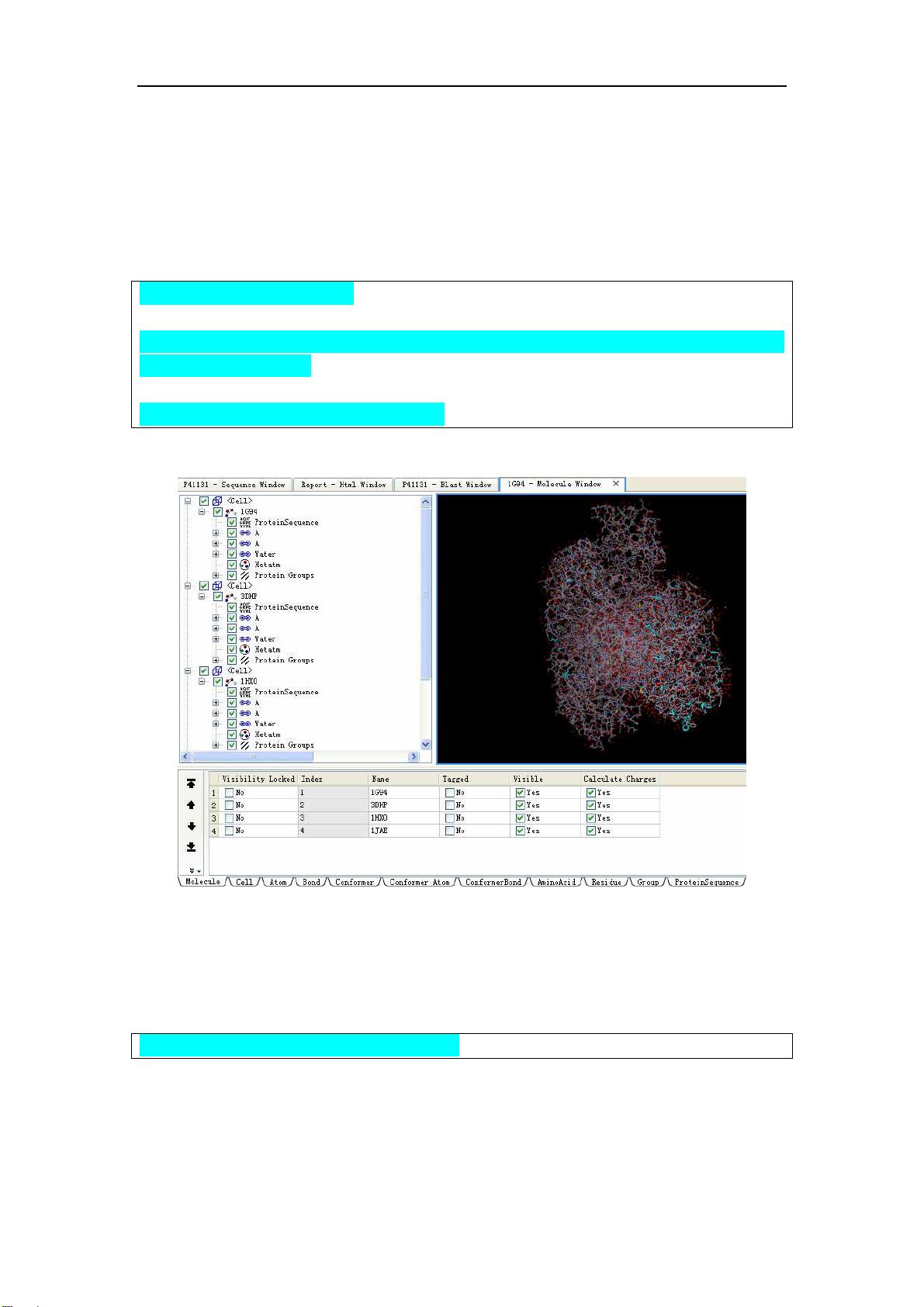
点击
点击点击
点击 P41131 - Blast Window.
点击
点击点击
点击 Map View tab, 按住
按住按住
按住 SHIFT 键同时点击前四个命中序列
键同时点击前四个命中序列键同时点击前四个命中序列
键同时点击前四个命中序列 1G94_A, 3DHP_A, 1HX0_A,
and 1JAE_A,
,,
,将其选中
将其选中将其选中
将其选中
点击
点击点击
点击右键
右键右键
右键,
,,
,选择
选择选择
选择“Load Selected Structures”
DS 将打开中一个为新的 3D 窗口(记为 1G94)。该窗口中包含了上述四个模板结构的 A 链
以及结构中的水分子和配体分子。
2.2 模板结构间的结构比对
模板结构间的结构比对模板结构间的结构比对
模板结构间的结构比对
序列保守性和结构保守性通常来说有所不同,所以序列比对的结果常常与结构比对的结
果不同。对于同源建模来说,在模板与 target 进行比对之前,最好能将模板基于其结构的相
似性先进行一次比对。
进行基于结构的序列比对之前,需要先调用每个模板的序列。
在菜单栏中
在菜单栏中在菜单栏中
在菜单栏中,
,,
,点击
点击点击
点击 Sequence | Show Sequence
DS 将打开一个名为 1G94 的新的序列窗口。该窗口中的序列没有经过任何的序列比对。
剩余111页未读,继续阅读
资源评论

weixin_41600466
- 粉丝: 0
- 资源: 1
上传资源 快速赚钱
 我的内容管理
展开
我的内容管理
展开
 我的资源
快来上传第一个资源
我的资源
快来上传第一个资源
 我的收益 登录查看自己的收益
我的收益 登录查看自己的收益 我的积分
登录查看自己的积分
我的积分
登录查看自己的积分
 我的C币
登录后查看C币余额
我的C币
登录后查看C币余额
 我的收藏
我的收藏  我的下载
我的下载  下载帮助
下载帮助

 前往需求广场,查看用户热搜
前往需求广场,查看用户热搜安全验证
文档复制为VIP权益,开通VIP直接复制
 信息提交成功
信息提交成功

