没有合适的资源?快使用搜索试试~ 我知道了~
资源推荐
资源详情
资源评论

4 受控分子动力学模拟(Steered Molecular Dynamics)
所谓受控分子动力学模拟(Steered Molecular Dynamics,SMD),就是指在进行分
子动力学模拟时,人为地给分子中的某个或某几个原子施加一个假想的外力,或者人为地
固定某个或某几个原子的位置。从而控制整个分子的行为。我们前面进行的动力学模拟都
是通过各种参数设置,尽量逼近蛋白质分子在溶液体系中的真实状态,以研究分子的各种
性质和行为。但受控分子动力学模拟却要用一个假想的外力干扰控制生物大分子的行为,
这是为什么呢?(需要查一下更多的SMD的应用实例,详细了解SMD究竟可以用于研究什
么问题,才能做出回答)
在下面的例子中,我们将首先固定泛素分子中一个原子的位置,然后用一个假想的
外力牵拉另一个原子。球形的泛素分子会因此而被逐渐拉开,最终成为伸展状态的肽链。
进行SMD时,我们需要用已经完成能量最小化和能量平衡,达到稳定状态的蛋白结
构。如果用含有扭曲、拉伸、变形构象的原始蛋白结构,我们将无法分清蛋白各部分的运
动是由于蛋白内部的形变张力引起的,还是由于SMD实验附加的外力造成的。因此,进行
SMD之前必须预先进行一次平衡态分子动力学模拟,获得稳定结构。
这里,我们使用2.4节球状水体分子动力学模拟输出的恢复文件(.restart)进行SMD。
恢复文件输出时,泛素已在水体中完成了能量最小化和能量平衡,达到了稳定状态。
4.1 除去水分子
为了节省计算时间,我们在进行本次SMD之前将除去体系中所有的水分子。但读者
必须要注意:在真正进行SMD实验的时候决不可以将水分子除去!
1、打开VMD,选择File→New Molecule菜单项,载入common目录下的文件ubq_ws.
psf。不要关闭窗口,此时窗口“Load file for:”一项应该显示“0:ubq_ws.psf”。再次单击按钮
Browser,找到1-2-sphere目录下的文件ubq_ws_eq.restart.coor,载入该文件。关闭Molec
ule File Browser窗口。
现在我们载入了2.4节球状水体动力学模拟时输出的恢复文件(.restart.coor)。
2、选择Extension → tk菜单项,打开tk,首先用cd命令改变当前目录至common目录
下,然后输入:
这样我们便在文件夹下新建了一个文件,储存已经
达到平衡态的蛋白质分子,但没有水分子。
、删除当前分子,但不要关闭。
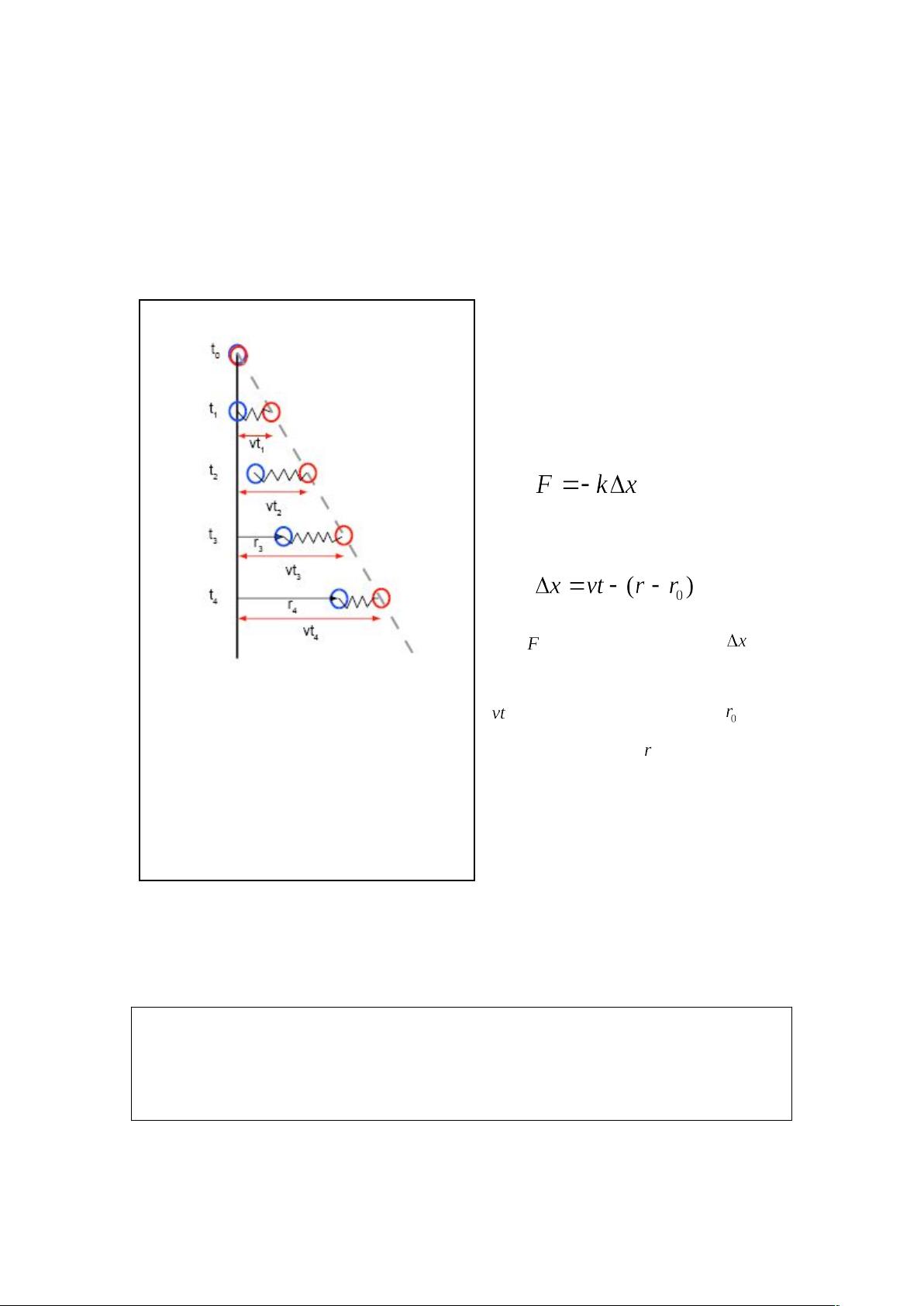
4.2 恒速牵拉
在这一节我们将使用恒速牵拉进行SMD动力学模拟。进行恒速牵拉时,我们需要首
先设定一个假想的原子作为施力原子,这个实际并不存在的原子就叫做假原子(dummy at
om)。假原子通过一根假想的弹簧与系统中真实存在的某个原子(称为 SMD原子)相连,
牵拉时,假原子以恒定的速度运动,因此
称这种牵拉方式为恒速牵拉。实际上被牵
拉原子(SMD原子)的速度不是恒定的
SMD原子所受拉力由弹簧的形变和弹性
系数决定,满足胡克定律:。
又有:
其中 是 SMD 原子所受的力, 是假
想弹簧的形变量。它等于假原子的位移
减去 SMD 原子的位移,其中 是 SM
D 原子的初始位置, 是 SMD 原子的当
前位置。
因此,SMD 原子的受力可以计算出
来,然后根据牛顿定律计算它的运动情况。
4.2.1 设定 SMD 原子和固定 原子
(Fixed atom)
NAMD使用pdb文件中的B因子一栏区别哪些原子是被固定的,哪些原子未被固定:如
果某个原子在该栏中的对应值是1(非0值即可),那么该原子被固定,在整个动力学模拟
过程中,它的空间坐标不会变化;反之如果为0,那么该原子不受影响。
知识链接:PDB文件的格式
使用写字板打开common目录下我们刚刚制作的ubq_ww_eq.pdb,可以看到文件的内
容分成几栏(column):
图 恒速牵拉的图示。图中SMD原子是
蓝色的,假原子(dummy atom)是红色的,
二者之间有一根假想的弹簧相连。假原子以
恒定的速度运动,弹簧发生形变后作用于S
MD原子,于是SMD原子开始运动。

在上图中,给我们提供有用信息的共有10栏数据,已在图中标注出:
(1)表示所指示为原子
(2)该原子序列号
(3)IUPAC标准格式的原子名称
(4)残基名称
(5)残基序列号
(6)原子的X坐标
(7)原子的Y坐标
(8)原子的Z坐标
()位置()
(10)温度因子或B因子(beta factor)
其中后两栏在动力学模拟的时候被NAMD用于标记两类特殊的原子:位置(Occupanc
y)栏用于标记SMD原子,B因子一栏用于标记固定原子(fixed atom)。

4.2.1 设定固定原子(fixed atom)和SMD原子
下面我们将使用VMD创建我们所需的pdb文件。我们在本例中将使用pdb文件中B因子
一栏(即温度因子)指定哪个原子将被固定,使用位置(occupancy)一栏指定哪个原子作
为SMD原子被牵拉。
1、在VMD中选择File→New Molecule 菜单项,单击Browse按钮找到common目录下
的文件ubq.psf,载入它。不要关闭Molecule File Browser窗口,注意Load file for 一项应当
显示1:ubq.psf。再次单击Browse按钮,载入common目录下的ubq_ww_eq.pdb。关闭Mole
cule File Browse窗口,在VMD图形窗口中应当可以看到没有水分子的泛素分子(图)。
图 载入除去水分子后的泛素分子
2、在VMD tk中输入以下命令,固定第一个氨基酸残基的α碳:
!"#$%&
!#

下面是对命令的解释:
新建了一个变量,它代表体系
中的所有原子。
所有原子在文件中的'栏(即)全部设为。
!"#$%& 新建一个变量
!,代表第一个氨基酸残基的α碳。
!# !所代表的原子——第一个氨基酸残基的(
碳的'栏被设置为#。这样)%会在分子动力学模拟时保持该原子固定。
同样地,我们还需要设定哪一个原子将被牵拉。前面提到过,被牵拉的原子就叫做
*原子。对于这一种原子,)%使用文件中的“位置”()一栏进行标
记。同样地,代表不受影响的原子,标记为#的原子将被牵拉。设置方法仍然是在+中输
入命令进行。
",-$%&
#
以下是对上述命令的解释:
当前文件中所有原子的“&一栏
设置为。
",-$%&新建了一个变
量,代表第,-个氨基酸(即最后一个氨基酸)的(碳。
#变量所代表的原子的
一栏设定为#,这样)%会在分子动力学模拟时将假想的力作用于该原子上。
完成上述设定之后,我们需要让输出我们设置好的文件。如果当前目录不是
,用命令改变当前目录到中,然后输入:
.回车后会在当前目录生成文件.,这就是我们进行*所
需的文件,它记录了泛素的结构,以及哪一个原子作为固定原子( !),哪一个
作为牵拉原子。
不要 关闭 ,将所有 窗口最 小化。 使用写 字板打 开 目录 下的文 件
.,注意打开时“文件类型”依然要选择“所有文件(//)”否则将看不到该文
件。在文件开头第六行即可找到固定原子——第一个氨基酸甲硫氨酸的(碳。这个原子的'
剩余26页未读,继续阅读
资源评论

loisirs7712
- 粉丝: 0
- 资源: 3
上传资源 快速赚钱
 我的内容管理
展开
我的内容管理
展开
 我的资源
快来上传第一个资源
我的资源
快来上传第一个资源
 我的收益 登录查看自己的收益
我的收益 登录查看自己的收益 我的积分
登录查看自己的积分
我的积分
登录查看自己的积分
 我的C币
登录后查看C币余额
我的C币
登录后查看C币余额
 我的收藏
我的收藏  我的下载
我的下载  下载帮助
下载帮助

 前往需求广场,查看用户热搜
前往需求广场,查看用户热搜安全验证
文档复制为VIP权益,开通VIP直接复制
 信息提交成功
信息提交成功

