没有合适的资源?快使用搜索试试~ 我知道了~
GSEA软件使用教程.pdf
1.该资源内容由用户上传,如若侵权请联系客服进行举报
2.虚拟产品一经售出概不退款(资源遇到问题,请及时私信上传者)
2.虚拟产品一经售出概不退款(资源遇到问题,请及时私信上传者)
版权申诉
温馨提示

试读
48页
数据库使用教程
资源推荐
资源详情
资源评论



◼
•
•
•
•
•
•
• 表型信息文件。
➢ 芯片数据额外需要 格式的芯片探针与基因名的注释文件。
01
◼
全称
• Molecular signatures database 分子标签数据库
特点
• 专门为GSEA富集分析提供数据集
• 涵盖了多样和广泛的基因集来源和类型,包括从原始文献中提取的基因标签,以及GO,KEGG,
TRANSFAC和L2L等网站的基因集。
• 通过人工收集和模型计算获得基因集,其他数据库仅搜集这些方法的一种
• 包含数据集最多
组成
• 官网提供了8个主要的数据集,包括hallmark gene sets、positional gene sets、curated gene
sets、motif gene sets、computational gene sets、GO gene sets、oncogenic signatures和
immunologic signatures
分析工具
• 官网提供了适用于全平台的GSEA可视化分析软件
更新
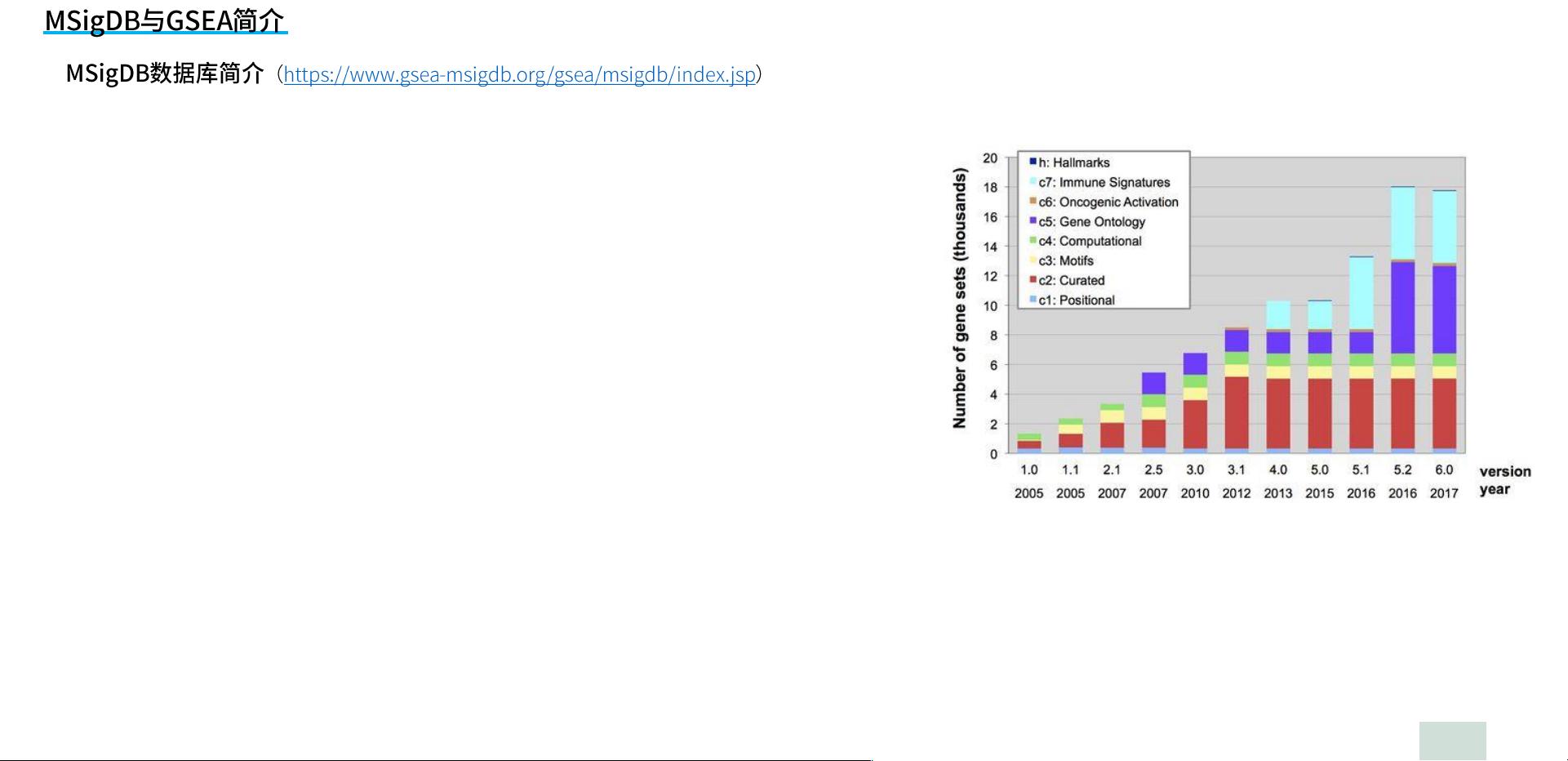
• 数据集和富集软件更新频繁,最近一次更新时间March 2020,MSigDB 数据最新版本v7.1
引用
• To cite your use of the Molecular Signatures Database (MSigDB), please reference
Subramanian, Tamayo, et al. (2005, PNAS 102, 15545-15550) and one or more of the
following as appropriate: Liberzon, et al. (2011, Bionformatics), Liberzon, et al. (2015, Cell
Systems), and also the source for the gene set as listed on the gene set page.
Summary statistics for MSigDB
来源:
software.broadinstitute.org/cancer/software/gsea/wiki/inde
x.php/MSigDB_Statistics
02

◼
1. H collection: Hallmark gene sets
• 作为MSigDB数据库和GSEA分析的起始数据集,Hallmark数据集搜集整理了特定分类的生物状态或过程,汇集了来自MSigDB v4.0数据集中C1到C6的经过整理筛选的
4000多个基因;是由多个已知基因集构成的超基因集。
2. C1 collection: Positional gene sets
• 该基因集注释来自于ENSEMBL BioMart (version 97) 的染色体和核型,反映了基因原始组装时的基因结构,小数被忽略掉。如 5q31.1和5q31.2、5q.31.3都代表5q31。
该基因集有助于鉴定染色体缺失或扩增、计量补偿、表观遗传及与区域相关的效应。
3. C2 collection:Curated gene sets
• 该基因集来源于多种在线的通路资源,生物医药文献和各领域专家的贡献。C2数据集包括两个子集:Chemical and genetic perturbations (CGP)和Canonical
pathways (CP)
➢ C2 子集CGP:基因集代表遗传和化学表达变化的标签。大多数CGP内容来自生物医药文献。过去的几十年里,芯片研究确定了多种重要生物和临床状态,包括癌症转移,
干细胞分类,耐药性。从芯片分析的文章附件中提取差异表达的基因集,这些基因集内容一般成对出现:用xxx_UP和xxx_DN的形式来命名基因集条目。CGP基因集的内
容主要来源于PubMed文献,原始数据一般公布在GEO或ArrayExpress。基因的命名和描述,与NCBI Entrez Gene数据库和NCBI PubChem Compound数据库一致。
• 华盛顿大学发表的芯片基因表达L2L数据库:
Newman JC, Weiner AM.
L2L: a simple tool for discovering the hidden significance in microarray expression
data. Genome Biol. 2005;6(9):R81. See also http://depts.washington.edu/l2l.
• 约翰霍普金斯大学药学院的MYC靶标基因数据库:
Zeller KI, Jegga AG, Aronow BJ, O'Donnell KA, Dang CV.
An integrated database of genes responsive to
the Myc oncogenic transcription factor: identification of direct genomic targets. Genome Biol. 2003;4(10):R69
03
剩余47页未读,继续阅读
资源评论

 Crazy_little_K2024-01-12资源和描述一致,质量不错,解决了我的问题,感谢资源主。
Crazy_little_K2024-01-12资源和描述一致,质量不错,解决了我的问题,感谢资源主。
小鸭文库
- 粉丝: 144
- 资源: 5904

下载权益

C知道特权

VIP文章

课程特权
开通VIP
上传资源 快速赚钱
 我的内容管理
展开
我的内容管理
展开
 我的资源
快来上传第一个资源
我的资源
快来上传第一个资源
 我的收益 登录查看自己的收益
我的收益 登录查看自己的收益 我的积分
登录查看自己的积分
我的积分
登录查看自己的积分
 我的C币
登录后查看C币余额
我的C币
登录后查看C币余额
 我的收藏
我的收藏  我的下载
我的下载  下载帮助
下载帮助

 前往需求广场,查看用户热搜
前往需求广场,查看用户热搜安全验证
文档复制为VIP权益,开通VIP直接复制
 信息提交成功
信息提交成功
