没有合适的资源?快使用搜索试试~ 我知道了~
2003554使用QIIME 2分析微生物组16S rRNA基因扩增子测序数据_final1
需积分: 0 11 下载量 61 浏览量
2022-08-08
21:10:20
上传
评论 2
收藏 720KB DOCX 举报
温馨提示

试读
23页
摘要:QIIME是目前微生物组扩增子分析领域使用最广泛的流程(软件),论文发表10年已经被引用超2万次。虽然QIIME的推出在微生物组数据分析领域具有里程碑意义
资源推荐
资源详情
资源评论

1
2 使用 QIIME 2 分析微生物组 16S rRNA 基因扩增子测序数据
3 Using QIIME 2 to Analysis Amplicon Sequencing of 16S rRNA Gene in
4 Microbiome
5 刘永鑫
1, 2, 3, #,
*,陈同
4, #
,钱旭波
5
,白洋
1, 2, 3, 6,
*
6
7
1
中国科学院遗传与发育生物学研究所,植物基因组学国家重点实验室,北京;
2
中国科学院大学,生物
8 互作卓越创新中心,北京;
3
中国科学院遗传与发育生物学研究所,中国科学院–英国约翰英纳斯中心植
9 物和微生物科学联合研究中心,北京;
4
中国中医科学院,中药资源中心,北京;
5
浙江中医药大学附属
10 金华中医院儿科,金华,浙江;
6
中国科学院大学现代农学院,北京
11 *通讯作者邮箱:yxliu@genetics.ac.cn;ybai@genetics.ac.cn
12
#
共同第一作者/同等贡献
13
14 摘要:QIIME 是目前微生物组扩增子分析领域使用最广泛的流程 (软件) ,论文发表 10
15 年已经被引用超 2 万次。虽然 QIIME 的推出在微生物组数据分析领域具有里程碑意义,
16 但是该流程已经无法满足快速发展的微生物组数据分析需求。全新开发的 QIIME 2 流程
17 采用 Python 3 编写,它结合最新算法,提供交互式图表,插件可扩展性强,能更好地
18 满足当前大数据和可重复分析的要求。然而,QIIME 2 无法在主流的 Windows 系统下
19 直接运行,且用户说明文档长达 10 多万字,对缺少生物信息背景的研究人员来说,学
20 会使用这样的流程仍然是个巨大挑战。本文将介绍软件安装方法和标准分析流程,方便
21 同行快速上手使用 QIIME 2 流程;我们对使用过程的中间步骤和参数进行解读,帮助用
22 户掌握参数优化方法,以获得更合理的结果;同时对软件安装和使用过程中的常见问题
23 和解决方案进行总结。本文介绍的微生物组分析指标和方法具体包括数据导入导出、特
24 征表生成、alpha 和 beta 多样性分析、物种组成分析、差异物种分析以及数据可视化等。
25 本文提供配套视频、分析代码、测序数据和预期结果,以方便同行学习和复现本文的分
26 析过程。
27 关键词:微生物组,扩增子,QIIME 2, 16S rDNA,可视化
28
29 仪器设备

30 1. ( 可选) 推荐使用计算服务器 ( 操作系统:Linux 主流发行版本, 如 CentOS
31 7+/Ubuntu 16.04+;CPU:4 核+;内存:16G+;硬盘:> 10 GB,且大于原始数
32 据大小 3 倍) ,网络访问畅通。
33 2. 个人电脑推荐 Windows 10 系统,内存 8G+。先在应用商店中安装 Linux 子系统 (如
34 Ubuntu 20.04 LTS) ,然后安装 QIIME 2;也可使用 VirtualBox 虚拟机运行 QIIME
35 2 镜像,但效率较低不推荐使用;Mac 系统可直接安装 QIIME 2。(可选) Windows
36 用户远程访问服务器需安装 XShell 或 Putty 等终端类软件,Mac 使用系统内置终
37 端即可远程访问计算服务器。
38
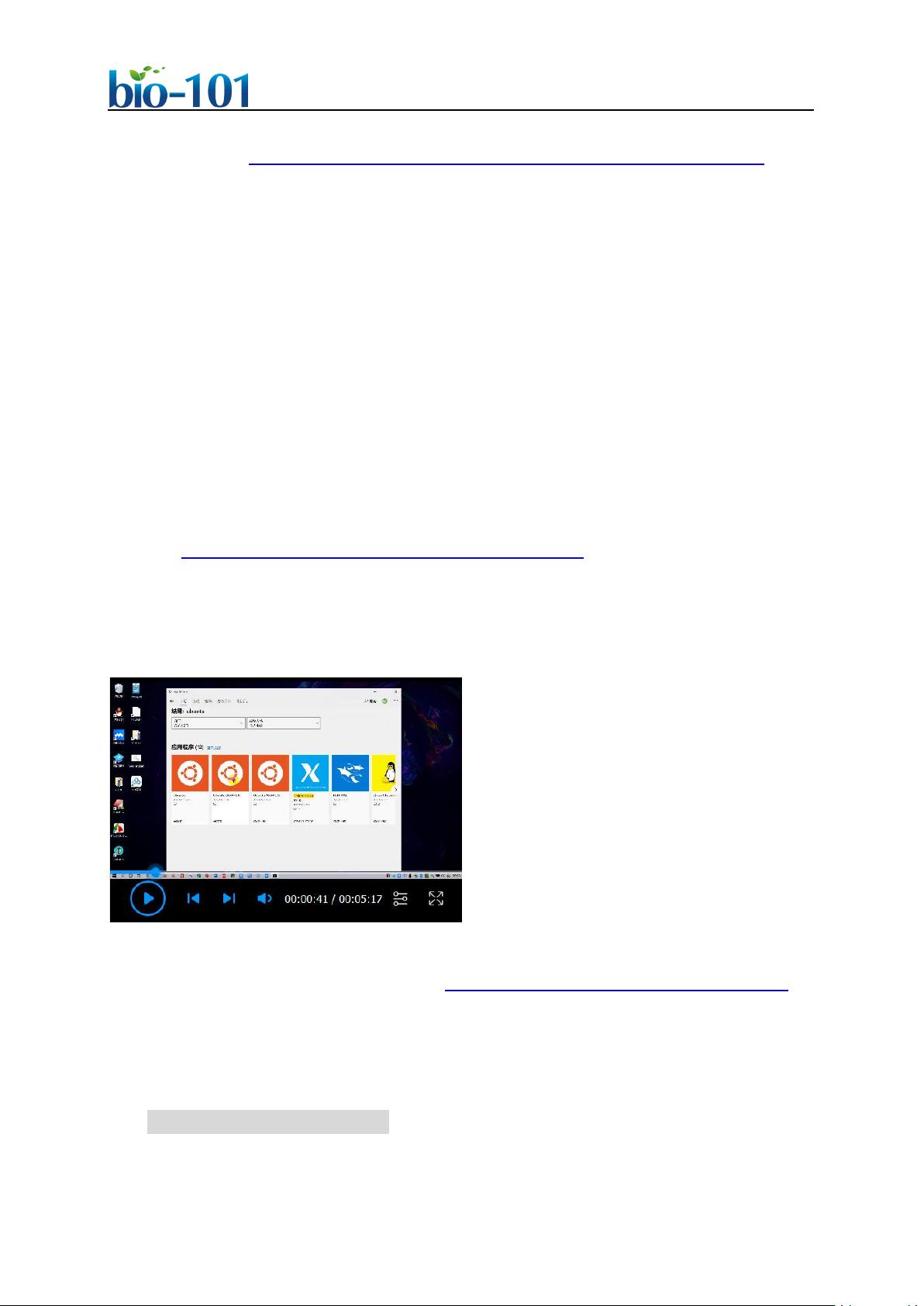
39 软件和数据库
40 1. QIIME 2 可运行的 Linux/Mac 四种环境任选其一:Linux 服务器 (推荐,适合大数
41 据) 、Windows 10 子系统 Ubutnu 20.04 LTS (推荐,适合小数据) 、Windows
42 中 VirtualBox 虚拟机中运行 Ubutnu 20.04 LTS (不推荐,适合小数据集,问题多
43 且效率低) 、Mac 系统 (不推荐,兼容性问题较多)
44 2. 软件管理器 Miniconda3 Linux 64-bit (Python 3.8) :https://conda.io/miniconda.ht
45 ml
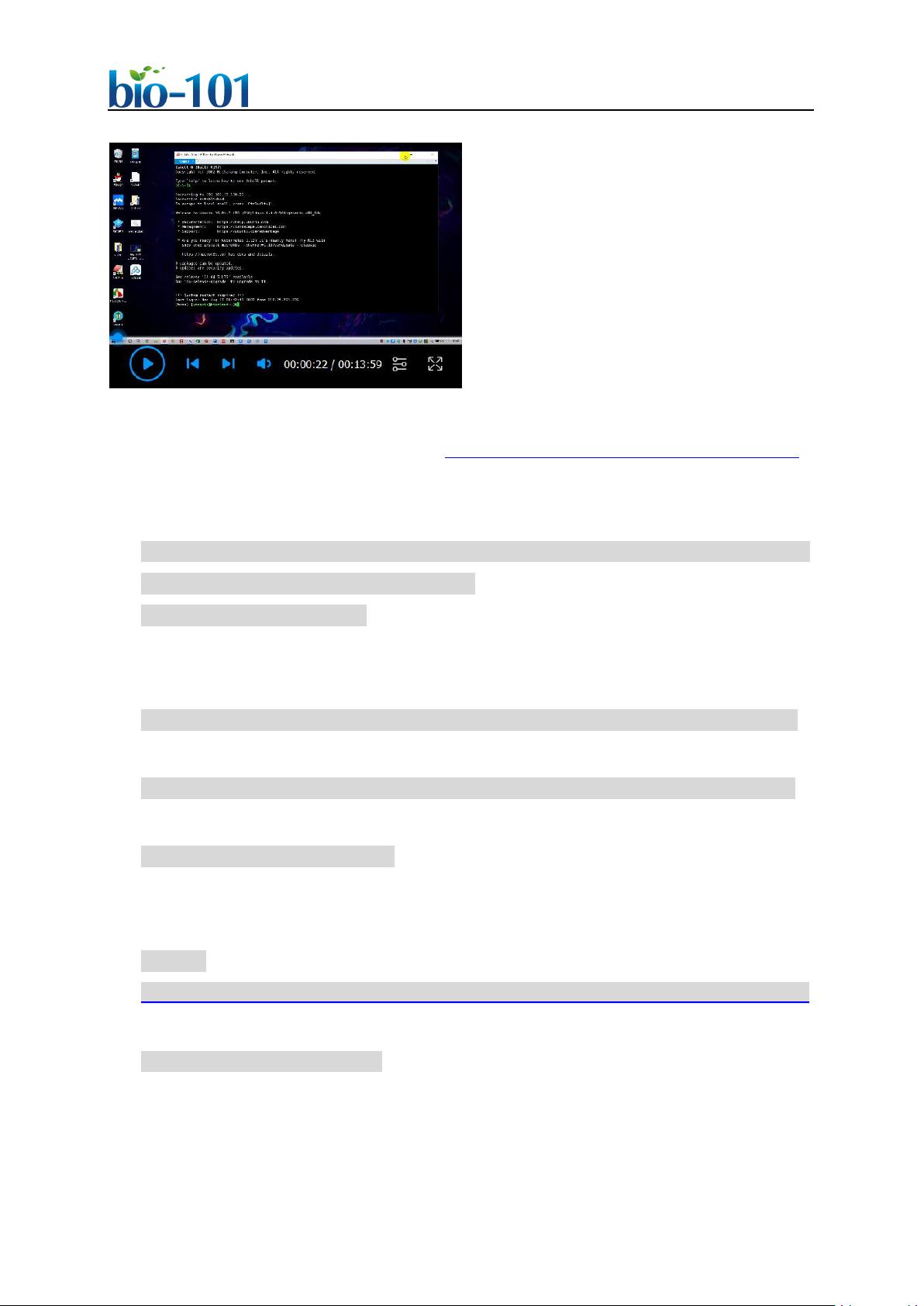
46 3. QIIME 2 (Bolyen et al., 2019) 发行版 2020.11:https://docs.qiime2.org/ (注:
47 QIIME 2 软件升级较频繁,如有更新,请使用最新版本,并在以下代码中替换 2020
48 .11 为最新的版本号即可,如遇问题请参考软件官方新版教程 https://docs.qiime2.or
49 g/)
50 4. GreenGenes 13.8 (McDonald et al., 2011) 物种分类数据库:ftp://greengenes.
51 microbio.me/greengenes_release/gg_13_5/gg_13_8_otus.tar.gz
52 5. 流程示例参考代码和结果文件详见:https://github.com/YongxinLiu/MicrobiomePro
53 tocol/blob/master/e2.QIIME2/,如示例代码为 QIIME2_Pipeline.sh
54 6. (可选) 远程文件传输工具 FileZilla 客户端 3.49.1+:https://filezilla-project.org/
55 7. (可选) Windows 远程访问服务器终端工具 Xshell 6.0.0197p+:https://www.netsar
56 ang.com/zh/free-for-home-school/
57 8. (可选) R 语言环境,下载适合自己系统的 4.0.2 版:https://www.r-project.org/
58 9. ( 可 选 ) R 语 言 开 发 环 境 , 用 于 执 行 流 程 , 下 载 适 合 自 己 系 统 的 RStudio
59 1.3.1056+:https://www.rstudio.com/products/rstudio/download/#download
60
61 软件安装和数据库部署
62 QIIME 2 不支持在 Windows 系统下直接安装。我们主要介绍远程访问 Linux 服务器和 Wi
63 ndows 10 下安装 Linux 子系统并使用 QIIME 2 两种方法,任选其一即可。
64 方法 1. 远程访问 Linux 服务器:Windows/Mac 用户安装 FileZilla 客户端,用于上
65 传测序数据至服务器或数据中心,也可下载分析结果本地查看。Windows 用户安装 Xshe
66 ll 用于远程访问服务器并开展分析,Mac 用户可使用系统自带 Terminal 中的 ssh 命令远
67 程访问服务器。
68 方法 2. Windows 10 的 1609 以后的版本可以安装 Linux 子系统:开始→Microsoft
69 Store→搜索“Ubuntu”→选择“Ubuntu 20.04 LTS”→安装。安装前的系统设置和常见问题
70 请阅读《Windows10 安装 Linux 子系统 Ubuntu 20.04LTS》。安装成功后可以在开始中
71 启动“Ubuntu 20.04 LTS”的命令行,也可选在 RStudio 中调置默认 Teriminal 为“Bash
72 (Windows Subsystem for Linux) ”,打开新终端即可使用。
73
74
75 视频 1. Windows 10 中应用商店安装 Ubuntu 20.04 LTS
76 视频在投稿时已经上传,在线观看链接:https://v.qq.com/x/page/d3138i66xpy.html
77
78 在 Linux 系统下,以 Miniconda3 软件和 Python3 虚拟环境安装 QIIME 2 流程;然
79 后下载 16S rRNA 基因数据库,建立物种分类器。
80
注:下文代码行添加灰色底纹背景,其中需要根据系统环境修改的部分标为蓝色。
81
82
83 视频 2. Conda 安装 QIIME 2 和训练分类器
84 视频在投稿时已经上传,在线观看链接:https://v.qq.com/x/page/s31384uumux.html
85
86 1. 安装 Miniconda3 Linux 64-bit (已安装请跳过)
87 wget -c https://repo.anaconda.com/miniconda/Miniconda3-latest-Linux-x86_64.sh
88 bash Miniconda3-latest-Linux-x86_64.sh
89 ~/miniconda3/bin/conda init
90 2. 下载 QIIME 2 流程安装软件列表
91 直接 wget 下载,但有时无法下载,详见常见问题 1。
92 wget -c https://data.qiime2.org/distro/core/qiime2-2020.11-py36-linux-conda.yml
93 3. Conda 新建环境安装 QIIME 2
94 conda env create -n qiime2-2020.11 --file qiime2-2020.11-py36-linux-conda.yml
95 进入工作环境
96 conda activate qiime2-2020.11
97 4. GreenGenes 数据库下载并导入
98 下载数据库文件 (greengenes) ,无法下载或下载慢见常见问题 2
99 wget -c
100 ftp://greengenes.microbio.me/greengenes_release/gg_13_5/gg_13_8_otus.tar.gz
101 解压
102 tar -zxvf gg_13_8_otus.tar.gz
103 使用 rep_set 文件中的 99_otus.fasta 数据和 taxonomy 中的 99_OTU_taxonomy.txt
104 数据作为参考物种注释。
105 导入参考序列
剩余22页未读,继续阅读
资源评论

白羊带你成长
- 粉丝: 21
- 资源: 329
上传资源 快速赚钱
 我的内容管理
展开
我的内容管理
展开
 我的资源
快来上传第一个资源
我的资源
快来上传第一个资源
 我的收益 登录查看自己的收益
我的收益 登录查看自己的收益 我的积分
登录查看自己的积分
我的积分
登录查看自己的积分
 我的C币
登录后查看C币余额
我的C币
登录后查看C币余额
 我的收藏
我的收藏  我的下载
我的下载  下载帮助
下载帮助

 前往需求广场,查看用户热搜
前往需求广场,查看用户热搜安全验证
文档复制为VIP权益,开通VIP直接复制
 信息提交成功
信息提交成功
