没有合适的资源?快使用搜索试试~ 我知道了~
论文笔记-Spatially informed cell-type deconvolution for spatial tran
需积分: 0 0 下载量 21 浏览量
2022-08-29
09:51:34
上传
评论
收藏 50.66MB DOCX 举报
温馨提示

试读
30页
论文笔记--Spatially informed cell-type deconvolution for spatial transcriptomics
资源推荐
资源详情
资源评论

论 文 笔 记 Spatially informed cell-type deconvolution for spatial
transcriptomics
(Nature Biotechnology 2022, 来自密西根大学)
论文摘要
许多空间分辨的转录组技术没有单细胞分辨率,而是从潜在的异质细胞类型的混合细胞中
测量每个点的平均基因表达。在这里,我们介绍了一种反褶积方法,即基于条件自回归的反褶
积(CARD),它将来自单细胞 RNA 测序(scRNA-seq)的细胞类型特异性表达信息与跨组织位置
的细胞类型组成的相关性结合起来。建模空间相关性可以使我们能够跨位置借用细胞类型的组
成信息,提高反褶积的准确性,即使有一个不匹配的 scRNA-seq 参考。CARD 还可以在未测
量的组织位置输入细胞类型组成和基因表达水平,从而构建一个精确的空间组织图,其分辨率
任意高于原始研究中的测量值,并可以在没有 scRNA-seq 参考的情况下进行反褶积。应用于
四个数据集,包括一个胰腺癌数据集,确定了多种细胞类型和具有不同空间定位的分子标记,
这些标记定义了胰腺癌的进展、异质性和区段化。
审阅人
占炎根
代码链接
www.xzlab.org/software.html
数据集
论文 code availability(很多)
核心总览
its ability to accommodate the spatial correlation structure in cell-type
composition across tissue locations by a conditional autoregressive (CAR)
modeling assumption
enable accurate and robust deconvolution of spatial transcriptomics data across
technologies with different spatial resolutions and in the presence of
mismatched scRNA-seq references.
impute cell-type compositions as well as gene expression levels on new locations

of the tissue
an extension of CARD is also capable of performing reference-free
deconvolution without an scRNA-seq reference.
背景介绍
动机
之前的 RCTD, stereoscope, cell2location 等方法都没有利用上细胞类型分布的空间相关
性。
算法实现
conditional autoregressive-based deconvolution (CARD),基于 a non-negative matrix
factorization model
表示单细胞数据中推断出的参考矩阵(每个元素代表某种基因在某种类型细胞
里的一个细胞中的平均表达水平),G 是基因种类数,K 是细胞类型数。
表示空间矩阵(每个元素代表在某个位置上某种基因的表达水平),N 是空间位
置数。

表示类型矩阵(每个元素代表某个位置上某种类型细胞的数量)。
用一个 non-negative matrix factorization 模型建模: 。
中元素限定为非负值。 是个残差矩阵,每个元素独立服从同样的正态分布
。
为 了 加 上 空 间 相 关 性 , 给 引 入 conditional autoregression (CAR) modeling
assumption: 。
代表 类型细胞在所有位置上的平均数量。
, 代表推断位置 处 的数量时,基于位置 处 的数量的权重。
代表该空间相关性信息的重要程度。
是个残差值。
用基于各对位置点之间的欧几里得距离的 Gaussian kernel function 来构建 ,特点是
善于建模随着距离增大而逐渐衰减的各种相关性模式。
Gaussian kernel : 。 是 欧 几 里 得 距 离 。
effectively characterizes the size of the focal expression patterns,影响很小,值设
为 0.1。
对 逐行标准化: , 。
为了使 和 服从 symmetric condition(即 ),设 , 是
个标量。
根据以上参数设置,基于 Brook's Lemma,可得 。(该推导过程在
论文附录里有详细说明)
是元素全是 1 的 维向量。
是 一 个 positive definite covariance matrix , 其 中
。
MVN 表示 multivariate normal distribution。
以上合起来就是 a factor model with a CAR modeling assumption on the latent
factors to induce spatial correlation across rows of V.
以上的超参数 也是由模型推断出的。
依照之前的研究结论, 从(0.01, 0.1, 0.3, 0.5, 0.7, 0.9, 0.99)这七个值里选,效果最
好的那个值为最终的取值。

设 服从一个 conjugate inverse-gamma distribution, 。
。依照之前的研究结论,设 ,#spots 应该是指空间位置总数。
对于 和 ,"we assigned the noninformative priors that are proportional to
one".
基于如下 log likelihood 来 infer :
Optimization for V:
详细推导过程见公式附录
Optimization for :
Optimization for :
Optimization for :
获得参考矩阵:
基因种类筛选:
选出单细胞数据和空间数据中都表达了的基因
选出表达水平高于平均表达水平 1.25-log-fold 的基因种类
剔除在一类细胞中表达变化性很高的基因种类,该变化性(称为 gene-specific
dispersion)用该类细胞该类基因的表达水平的方差除以均值来体现。剔除掉
gene-specific dispersion 最高的 1%的基因种类。
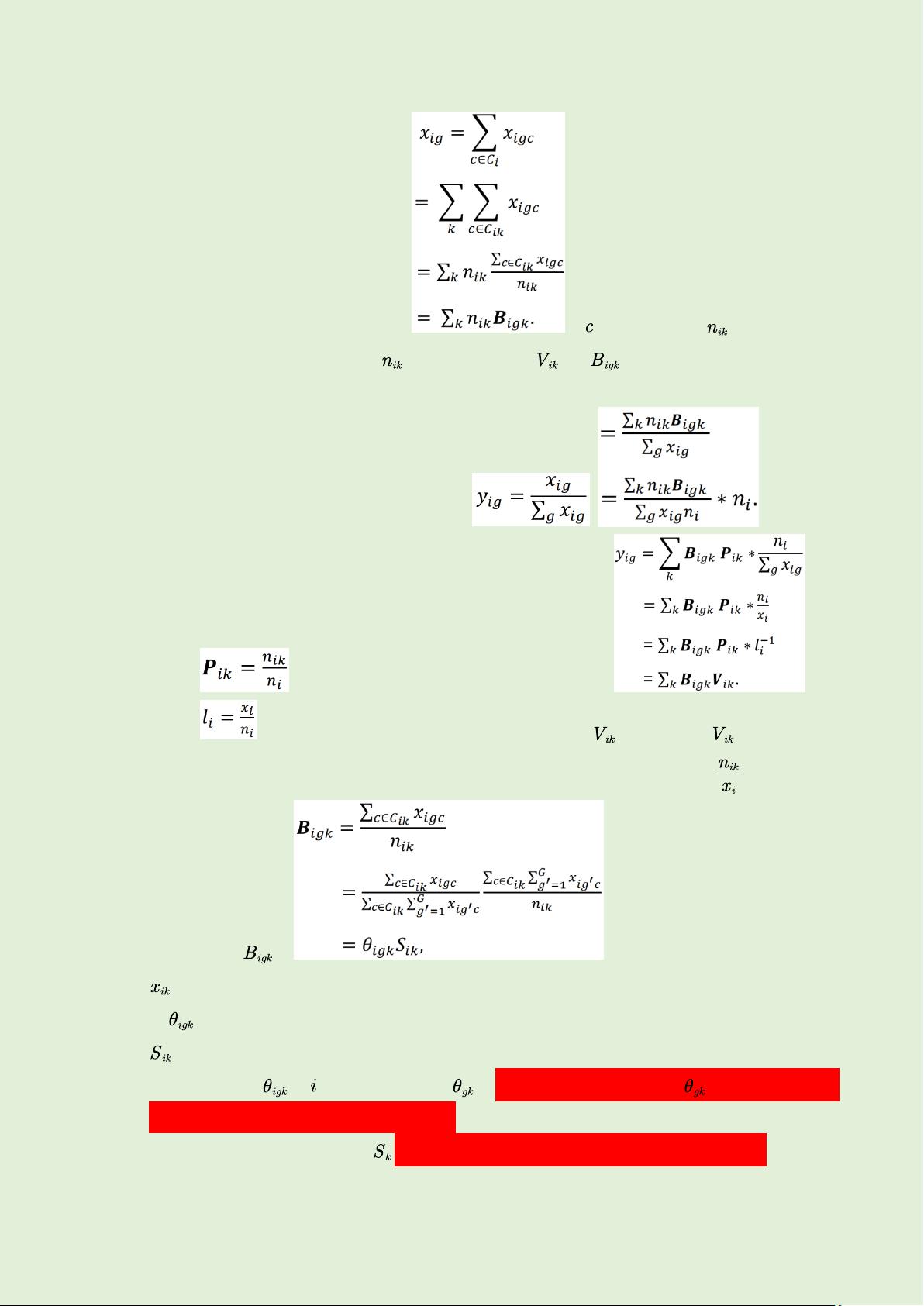
位置 i 处基因 g 的数量可表达为 。 表示细胞 c。 表示位置 i 类
型 k 的细胞数量(实际上这个 等同于之前说的 )。 就是位置 i 来自细胞类型 k
的基因 g 在一个细胞中的平均表达值。
相对值(基因 g 在位置 i 的数量占比):
设 ,指类型 k 细胞在 i 位置的数量占比,则 。其
中 ,指每个细胞的平均基因总数量。这里的 与之前说的 含义不同!!
是位置 i 处类型 k 的细胞总数除以位置 i 处所有类型的基因总数( )。
进一步处理 : ,第二行新引入的一项含义是
,即位置 i 来自类型 k 细胞的所有种类基因的数量。
则 则代表位置 i 处类型 k 细胞中基因 g 的相对数量占比。
代表位置 i 处类型 k 细胞中一个细胞里的平均基因总数量。
设空间数据中 在 维度上的均值为 ,并且和单细胞数据中的 相等(感觉这个
假设有点太强了,应该考虑一些误差)。
同理假设空间数据中的均值 和单细胞数据中的相等(假设也有点太强了)
剩余29页未读,继续阅读
资源评论

齑殷_
- 粉丝: 1
- 资源: 1
上传资源 快速赚钱
 我的内容管理
展开
我的内容管理
展开
 我的资源
快来上传第一个资源
我的资源
快来上传第一个资源
 我的收益 登录查看自己的收益
我的收益 登录查看自己的收益 我的积分
登录查看自己的积分
我的积分
登录查看自己的积分
 我的C币
登录后查看C币余额
我的C币
登录后查看C币余额
 我的收藏
我的收藏  我的下载
我的下载  下载帮助
下载帮助

 前往需求广场,查看用户热搜
前往需求广场,查看用户热搜安全验证
文档复制为VIP权益,开通VIP直接复制
 信息提交成功
信息提交成功
