没有合适的资源?快使用搜索试试~ 我知道了~
1RNAseq质量控制.docx
1.该资源内容由用户上传,如若侵权请联系客服进行举报
2.虚拟产品一经售出概不退款(资源遇到问题,请及时私信上传者)
2.虚拟产品一经售出概不退款(资源遇到问题,请及时私信上传者)
版权申诉
温馨提示

试读
11页
1RNAseq质量控制.docx
资源推荐
资源详情
资源评论

RNA-seq 质量控制
1 建库流程
1.1 Total RNA 样品检测
1.1.1 琼脂糖凝胶电泳分析 RNA 降解程度以及是否有污染
一句话总结:琼脂检测主要观察 28s 和 18s。判断 RNA 好坏的标准是28s,18s 是否清晰,尤其是 28S
亮度比 18s 亮度大
28s,主要是剪切前的前体 RNA,主要包括不均一核 RNA(未剪切成熟的 mRNA 前体)和主要是 28s,
18s,5s 的前体转录子。前体存在于细胞核(然后加工剪切成 28s,18s,5s 和成熟的小片段的 mRNA。
这些成熟的 RNA 进入到胞浆。有功能的 mRNA 是存在于胞浆中的成熟的 mRNA,前体 mRNA 是没有
翻译功能的(蛋白质翻译机器,核单倍体是位于胞浆中的)。真正成熟的 mRNA,主要集中在 28s 和 18s
之间的荧光背景(一般每条基因 mRNA 量很少,所以,整体一般看不到明显带).如果 28s 只是比 18s 稍
高,或者亮度差不多,即使条带清晰,也已经提示部分降解了。大片段开始降解,从 28s 降解到 18s 最
后降解到 5s。这样降解过程中,28s 减少,18s 增多,28s:18s 比例就会下降。如果最容易降解的 28s
都没有降解,(从比例推断),那么更难降解的 mRNA,就推理出肯定是完好的了。
泳道:
1 2 3 4 5 6 7 8 9
这张图片就是一个离心柱子提取 RNA 的不同降解情况的典型例子。
泳道 1,5,6,7,8,9 部分降解了,所以 28s 是首先降解,28s 条带变淡,而部分降解首先是降解成较小的 18s
左右的片段,所以 18s 条带明显变粗,造成 28s:18s 的比例竟然小于 1 了。然后在不该看到条带或者应
该是很弱的 5s 位置,出现了较明显的 5s 大小的降解带。
3,4 是完全降解了,28s,18s 已经基本降解光了。两条带都看不见了。最后降解成的小片段正好和 5s 大
小一致,所以在 5s 位置看到了大量的一条浓浓的降解小片段,和 5s 一样大小。
2 就是完全正常提取的 RNA,大家可以看到 28s:18s 比例大约是 2:1,5s 位置也基本见不到带。这就说明完
全正常,无降解。
(2) Nanodrop 检测 RNA 的纯度(OD260/280 比值)
一句话总结:260/280 大约在 2.0 而 260/230 ration 在 2.0-2.2.
OD260 代表核酸的吸光度,OD280 代表蛋白质的吸光度。280、320、230、260nm 下的吸光度分别代
表了核酸、背景(溶液浑浊度)、盐浓度和蛋白等有机物的值。A230 测定其它碳源物质,如酚,糖类
等;A260 是核酸的吸收峰测 RNA 和 DNA,引物等的浓度用的;A280 是蛋白质的吸收峰。
一般的,我们只看 OD260/OD280(Ratio,R)——1.8~2.0 时,我们认为 RNA 中蛋白或者时其他有
机物的污染是可以容忍的,不过要注意,当用 Tris 作为缓冲液检测吸光度时,R 值可能会大于 2(一般

应该是<2.2 的)。当 R<1.8 时,溶液中蛋白或者其他有机物的污染比较明显,你可以根据自己的需要决
定这份 RNA 的命运。当 R>2.2 时,说明 RNA 已经水解成单核酸了。 纯 RNA 的 A260/A280 的比值
为 2.0。
OD260/OD230 的比值还表明 RNA 的纯度——其值 <2.0 表明裂解液中有亚硫氰胍和β-巰基乙醇残
留,其值 >2.4,需用乙酸盐,乙醇沉淀 RNA。
(3) Qubit 对 RNA 浓度进行精确定量
一句话总结:RNA-seq 测序需要至少 300 ng 总 RNA
(4) Agilent 2100 精确检测 RNA 的完整性
一句话总结:2100 RIN 值高好,样品间 RIN 值相差 1-1.5 最好。
Agilent 2100 对文库的 insert size 进行检测,RIN 值反应的是样品的降解。RIN=RNA integrity
number,即 RNA 分子完整数,从 0-10,直接反应了 RNA 质量的好坏,此数值越大表明 RNA 质量
越好越完整。
1.2 建库流程
1.2.1 ssRNA-seq 建库(针对长非编码 RNA 分析)
RNA 检测合格后,通过 epicentre Ribo-Zero
TM
试剂盒去除 rRNA(可以拿到非 polyA 的转录本)随后
加入 fragmentation buffer 将 RNA 打断成 150-200bp 短片段 150-200bp,以短片段 RNA 为模板,用
六碱基随机引物(random hexamers)合成一链 cDNA,然后加入缓冲液、dNTPs(dUTP、dATP、
dGTP 和 dCTP)和 DNA polymerase I 合成二链 cDNA,随后利用 AMPure XP beads 纯化双链
cDNA。纯化的双链 cDNA 再进行末端修复、加 A 尾并连接测序接头,然后用 AMPure XP beads 进行
片段大小选择。之后用 USER 酶降解含有 U 的 cDNA 第二链,最后进行 PCR 富集得到链特异性 cDNA
文库。
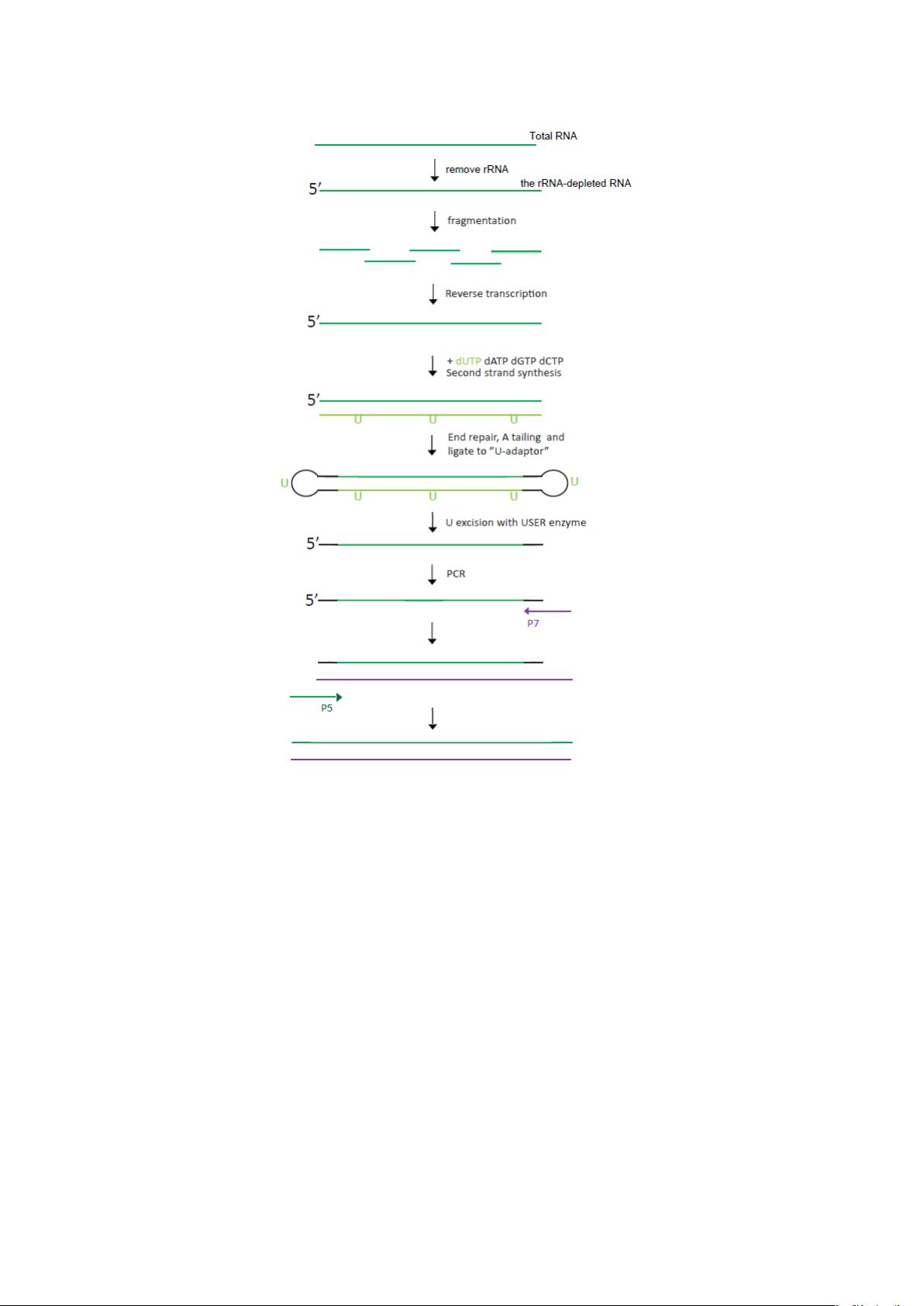
图:lncRNA 建库
1.2.2 小 RNA 建库
样品检测合格后,使用 Small RNA Sample Pre Kit 构建文库,利用 Small RNA 的 3’ 及 5’
端特殊结构( 5’ 端有完整的磷酸基团, 3’ 端有羟基),以 total RNA 为起始样品,直接将 Small
RNA 两端加上接头,然后反转录合成 cDNA 。随后经过 PCR 扩增, PAGE 胶电泳分离目标 DNA
片段,切胶回收得到的即为 cDNA 文库。
剩余10页未读,继续阅读
资源评论

 王景8652023-08-30这个资源总结的也太全面了吧,内容详实,对我帮助很大。
王景8652023-08-30这个资源总结的也太全面了吧,内容详实,对我帮助很大。
chenlu0528
- 粉丝: 2
- 资源: 48万+

下载权益

C知道特权

VIP文章

课程特权
开通VIP
上传资源 快速赚钱
 我的内容管理
展开
我的内容管理
展开
 我的资源
快来上传第一个资源
我的资源
快来上传第一个资源
 我的收益 登录查看自己的收益
我的收益 登录查看自己的收益 我的积分
登录查看自己的积分
我的积分
登录查看自己的积分
 我的C币
登录后查看C币余额
我的C币
登录后查看C币余额
 我的收藏
我的收藏  我的下载
我的下载  下载帮助
下载帮助

 前往需求广场,查看用户热搜
前往需求广场,查看用户热搜安全验证
文档复制为VIP权益,开通VIP直接复制
 信息提交成功
信息提交成功
