个人初步总结
个人详细使用:
BEAUti
1、File-—Import Data—翻开 NEXUS(beauti 软件的 NEXUS 文件与 PAUP 软件的有不同)
文件翻开后显示为
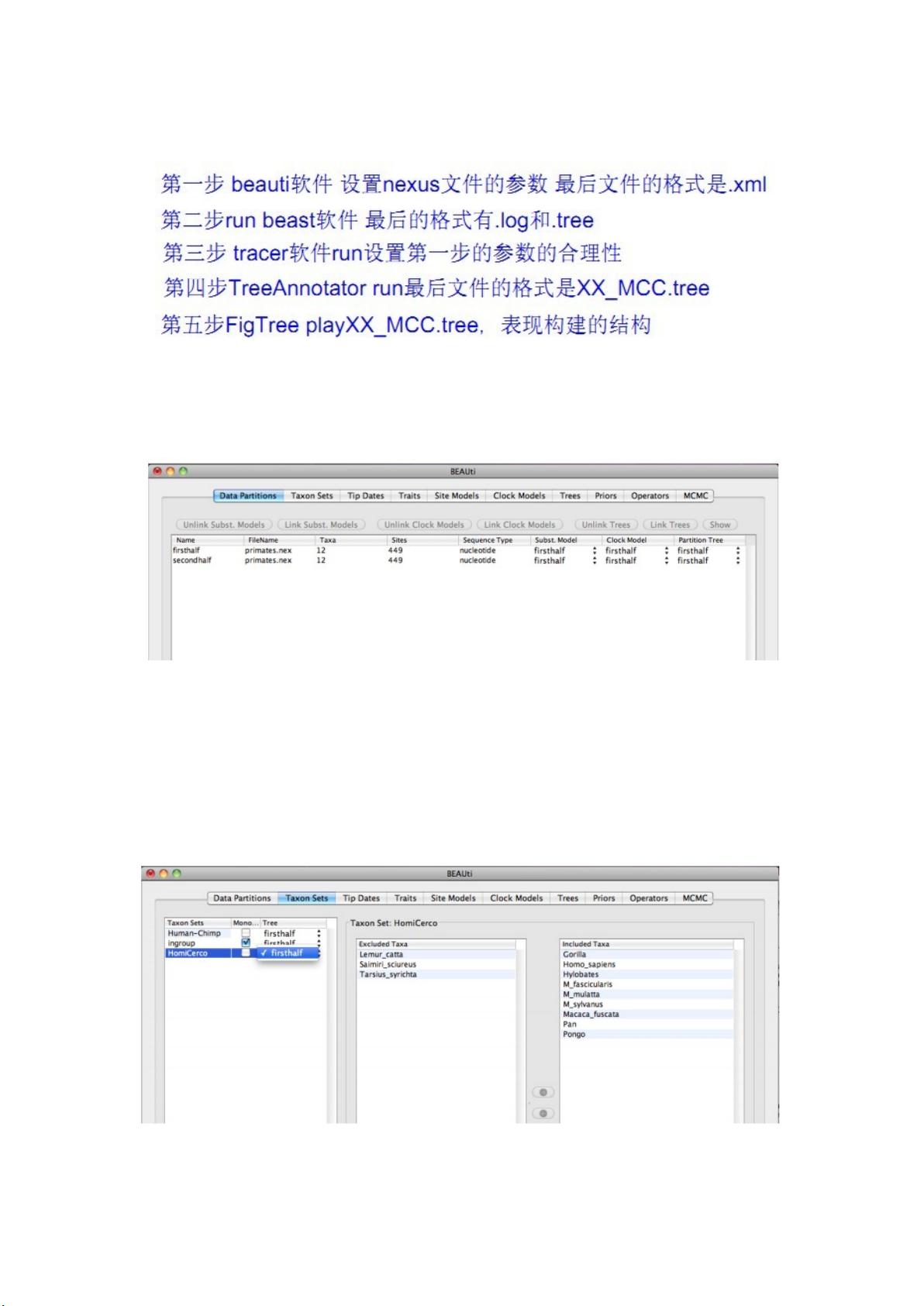
2、选择Taxon Sets通过建立一套定义子集分类,这个窗口允许你建立分类单元内的子集序列
数据。这也允许你去记录每个分类tMRCA子集最近的共同祖先,设置分布在相应分歧时间的
分歧倍。最后tMRCAs在日志文件中应按单位相同规定你的DNA序列。这些分类单元可以代
表不同的物种子集分析地理上孤立的多种群或者在一个物种。值得注意的是,建立一个分类
单元不保证该子集集团将能够对其它属种单源推理分析。
单击“+〞在左下角,创立几个分类群,重命名他们。在另一个中你可以看到一些有用的分
类群,选择你所需要的分类群然后单击绿色的按钮,确使在 MCMC 分析的时候保持单源。
最后可以得到类似:
3、选择 substitution model 这里主要是模型的选择
substitution model 中主要为三个模型 HKY GTR TN93 根据模型构建来选择